Définition de l'ADN mitochondrial
Divers / / July 04, 2022
définition du concept
Le génome mitochondrial est une petite molécule circulaire fermée à double hélice de 16 569 paires de bases (pb) qui n'est héritée que des mères aux fils et aux filles (rarement). cas d'hétéroplasmie), il n'y a donc pas de recombinaison génétique au moment de la conception, elle évolue aussi exclusivement par accumulation de mutations dans le Météo.






Lic. en anthropologie physique
Le taux élevé de mutation du génome mitochondrial (10 à 20 fois celui du ADN nucléaire, en termes de gènes ayant des fonctions comparables) est utile pour différencier les populations qui au fil du temps ont été biologiquement liés, cependant, leur taux de mutation peut être si rapide que des phénomènes de mutation peuvent se produire. rétromutation. Le taux de évolution La moyenne de cette molécule a été calculée à partir d'espèces pour lesquelles les temps de divergence par rapport aux restes fossiles étaient disponibles, et à partir de données biodémographiques ou protéiques; le résultat donne 1-2% par million d'années, valable pour différents ordres.
Cet ADN particulier fonctionne comme un outil pour rechercher la parenté biologique entre populations car leurs propriétés permettent d'élucider les relations entre populations qui ont divergé ces derniers temps, sans avoir à prendre en compte les phénomènes de recombinaison et en ajoutant une dimension temporaire; Pour cela, il faut garder à l'esprit ce qui suit: deux individus dont l'ancêtre commun a été une femme auront molécules d'ADN mitochondrial aussi différentes que le temps s'est écoulé depuis la séparation des ancêtre.
Haplogroupes pour la classification de l'ADN mitochondrial dans la distribution géographique
Certaines régions de l'ADN peuvent être très similaires les unes aux autres, ce qui permet à leur classification dans le même groupe, appelé haplogroupe. Par exemple, Torroni et al (1993) ont typifié les lignées mitochondriales fondatrices pour le continent américain, les qui a reçu la dénomination des haplogroupes A, B, C et D, selon des mutations ponctuelles de la séquence mitochondriale. Ces mutations créent différents sites de clivage pour des enzymes spécifiques, comme décrit ci-dessous: dans la lignée A, il y a le site cutoff 663 pour l'enzyme HaeIII, la lignée C est caractérisée par le site 13259 pour HincII, dans la lignée D le site 5176 est reconnu pour AluI; cette identification est faite à partir de polymorphismes de longueur de fragment (RFLP). Dans le cas de la lignée B, il y a une délétion de 9 paires de bases en position 8272-8289.
La répartition géographique de chaque lignage a été décrite comme suit: le lignage A est prédominant sur le continent américain et surtout en Amérique du Nord; cependant, cet haplogroupe est également attribué aux populations mésoaméricaines. Les lignées C et D apparaissent principalement en Amérique du Sud; la lignée B se trouve dans la région nord et sud de la côte du Pacifique, et Kemp et al (2010) la propose comme une lignée caractéristique de la famille Yuto-Aztecan et sud-ouest des États-Unis
De plus, il existe des mutations partagées entre individus d'un même haplogroupe, ce qui a permis de décrire des haplotypes (ou sous-lignages) spécifiques de certaines populations. La figure 1 montre les régions de l'ADN mitochondrial qui contiennent les mutations pour reconnaître chaque lignée.
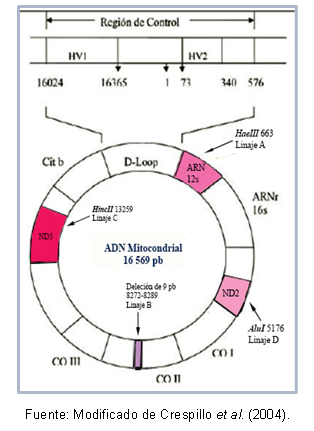
Figure 1. Régions d'ADN mitochondrial caractérisant chaque lignée fondatrice américaine.
Pendant quelques années, seules ces quatre lignées ont été reconnues jusqu'à ce que l'haplogroupe X soit inclus pour les populations du nord du continent; qui est aussi éloignée des populations européennes. Les lignées précédentes ont une correspondance avec les populations asiatiques, bien qu'elles soient observées moins fréquemment que sur le continent américain; les lignées A, B et C ne se trouvent pas chez les Africains et les Caucasiens modernes; et la lignée D existe également en Afrique, mais associée à d'autres sites de restriction. Avec ce qui précède, on pourrait dire que ces haplogroupes caractérisent les populations américaines et donc leur étude est adéquate en termes de peuplement et de migrations (anciennes et récentes).
distances génétiques
La façon d'établir des similitudes ou des différences génétiques entre des populations est d'utiliser des distances génétiques, qui peuvent avoir une explication historique, puisqu'ils changent (augmentent ou diminuent) au fil des générations, et peuvent nous conduire à des événements de l'histoire d'une Ville par exemple: lors d'une grande migration ou d'un contact entre deux cultures, avec ce calcul nous pouvons discerner quels mécanismes sont entrés en action pour nous donner tel ou tel résultat.
La dérive génétique et le flux de gènes ont à voir avec la facilité avec laquelle un groupe, dans ce cas des êtres humains, doit se déplacer au sein d'un groupe. territoire et d'entrer en contact avec d'autres groupes. Ainsi, l'isolement géographique est la distance génétique qui augmente avec l'augmentation de la distance géographique entre les groupes humains.
Hypothèse de la diversité de l'ADN mitochondrial
Pour expliquer le la diversité dans les lignées mitochondriales fondatrices en Amérique, il y a deux hypothèse: que ce continent a été colonisé par de multiples événements venus de la Béringie, ou qu'une fois la migration effectuée, des changements évolutifs se sont produits après la colonisation. Deux voies d'entrée de ces variations sur le continent sont également expliquées, la première propose que les quatre haplogroupes fondateurs sans variations, c'est-à-dire chacun avec une haplotype racinaire, elles auraient pu arriver juste après le dernier maximum glaciaire ou un peu avant, avec des dates d'il y a 21 mille à 19 mille ans et auraient suivi une route côtière par le Pacifique; la deuxième proposition suggère que ces variations intra-haplogroupes existaient déjà en Béringie et ont été amenées au sud du continent américain mais leur entrée aurait été exactement à la fin du dernier maximum glaciaire pour que les routes à l'intérieur du continent soient déjà libres, alors l'entrée de ces groupes humains serait il y a 19 mille années. Il existe également une grande diversité d'haplogroupe A et un temps de coalescence pour celui-ci plus court que le reste (17 000 ans).
L'explication la plus probable à cela est que cela est dû à des expansions secondaires de l'haplogroupe A de la Béringie, longtemps après la fin du dernier maximum glaciaire. Malgré l'écart concernant le moment de l'entrée de l'homme dans les Amériques, les études génétiques ont apporter quelques éclaircissements, car ils soutiennent l'hypothèse qu'il y avait des groupes humains sur le continent américain avant Clovis; et on constate qu'il y a une séparation entre les ancêtres de l'Asie du Nord-Est il y a 25 à 35 mille ans et l'entrée en Amérique il y a 15 à 35 mille ans. La figure 2 montre les itinéraires des haplogroupes mitochondriaux dans le monde et le temps de divergence dans les années avant le présent.
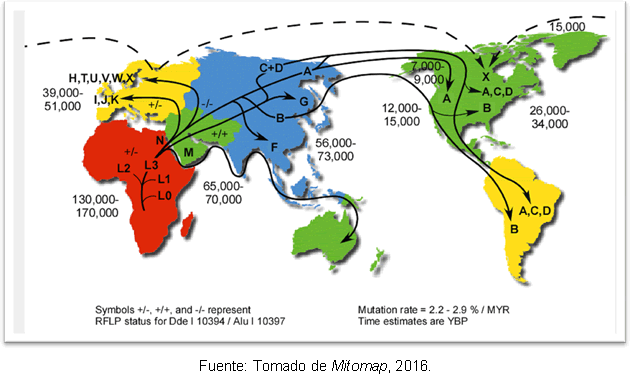
Figure 2. Carte des différentes voies de dispersion des lignées mitochondriales
Importance de la phylogéographie dans l'étude génétique et les données sur les gènes mitochondriaux
Il existe un outil très utile pour l'analyse génétique; la phylogéographie. Ce sont les premières applications des études moléculaires, et avec elles on cherche à pouvoir déterminer les relations phylogénétiques et spatiales entre les séquences nucléotidiques, en l'occurrence l'ADN mitochondriale. La distribution spatiale peut ressembler à un modèle temporel, c'est-à-dire que les séquences d'ADN les plus éloignées géographiquement devraient être les plus génétiquement différentes, ainsi que les séquences d'ADN qui ont divergé il y a longtemps devraient également être les plus différentes génétiquement. Ainsi, des populations géographiquement éloignées, avec peu ou pas de flux de gènes entre elles, accumuleraient des différences dues à la dérive génétique et à la mutation, même par sélection; mais des situations peuvent survenir qui ne permettent pas la dérive, comme un ou plusieurs effets fondateurs ou d'autres modèles de flux de gènes.
Les données fournies par les gènes mitochondriaux ont été parmi les plus utiles dans la recherche en phylogéographie en raison de la caractéristique que ces gènes ont de ne pas se recombiner et par conséquent ils montrent une lignée phylogénétique beaucoup plus claire que beaucoup gènes nucléaires. La taille effective de la population calculée avec les gènes mitochondriaux (et avec le chromosome Y fonctionnant de manière similaire) est d'environ un quart de celle calculée pour les gènes mitochondriaux. gènes nucléaires, alors la divergence se produit presque quatre fois plus vite qu'avec les gènes nucléaires, ce taux rapide de divergence (et de flux de gènes) peut provoquer la modèle d'hérédité observé dans ces gènes uniparentaux est différent des phylogénies obtenues avec des gènes nucléaires (qui représentent la majorité du pool de gènes dans un individu).
Références
Achilli, A., Perego, U. A., Bravi, C. M., Coble, M. D., Kong, Q.-P., & et al. (2008). La phylogénie des quatre haplogroupes panaméricains d'ADNmt: implications pour les études évolutives et pathologiques. PLoS ONE, 3(3), e1764.Cavalli-Sforza, L. L (2000). Gènes, peuples et langues (1ère édition in Pocket Library ed.). Barcelone, Espagne: Éditorial critique.
Rebato, E., Susanne, C., & Chiarelli, B. (Modifications.). (2005). Comprendre l'Anthropologie Biologique: évolution et biologie humaine. Parole divine.
Torroni, A., Schurr, T. G., Cabell, M. F, Brun, M. D, Neel, J. V., Larsen, M., et al. (1993). Affinités asiatiques et rayonnement continental des quatre ADNmt amérindiens fondateurs. Le Journal américain de génétique humaine, 53(3), 563.
(2022). ADN mitochondrial, Institut national de recherche sur le génome humain.
-Référence schématique de l'ADN mitochondrial-
Crespillo, M., Paredes, M., Arimany, J., Guerrero, L. et Valverde, J. (2004). Guerre civile espagnole (1936-1939): identification de restes humains provenant de fosses communes en Catalogne par analyse de l'ADN mitochondrial. À propos d'un cas. Cahiers de médecine légale (38), 37-46.


